 Maxquant使用说明.docx
Maxquant使用说明.docx
- 文档编号:4211339
- 上传时间:2022-11-28
- 格式:DOCX
- 页数:10
- 大小:42.96KB
Maxquant使用说明.docx
《Maxquant使用说明.docx》由会员分享,可在线阅读,更多相关《Maxquant使用说明.docx(10页珍藏版)》请在冰豆网上搜索。
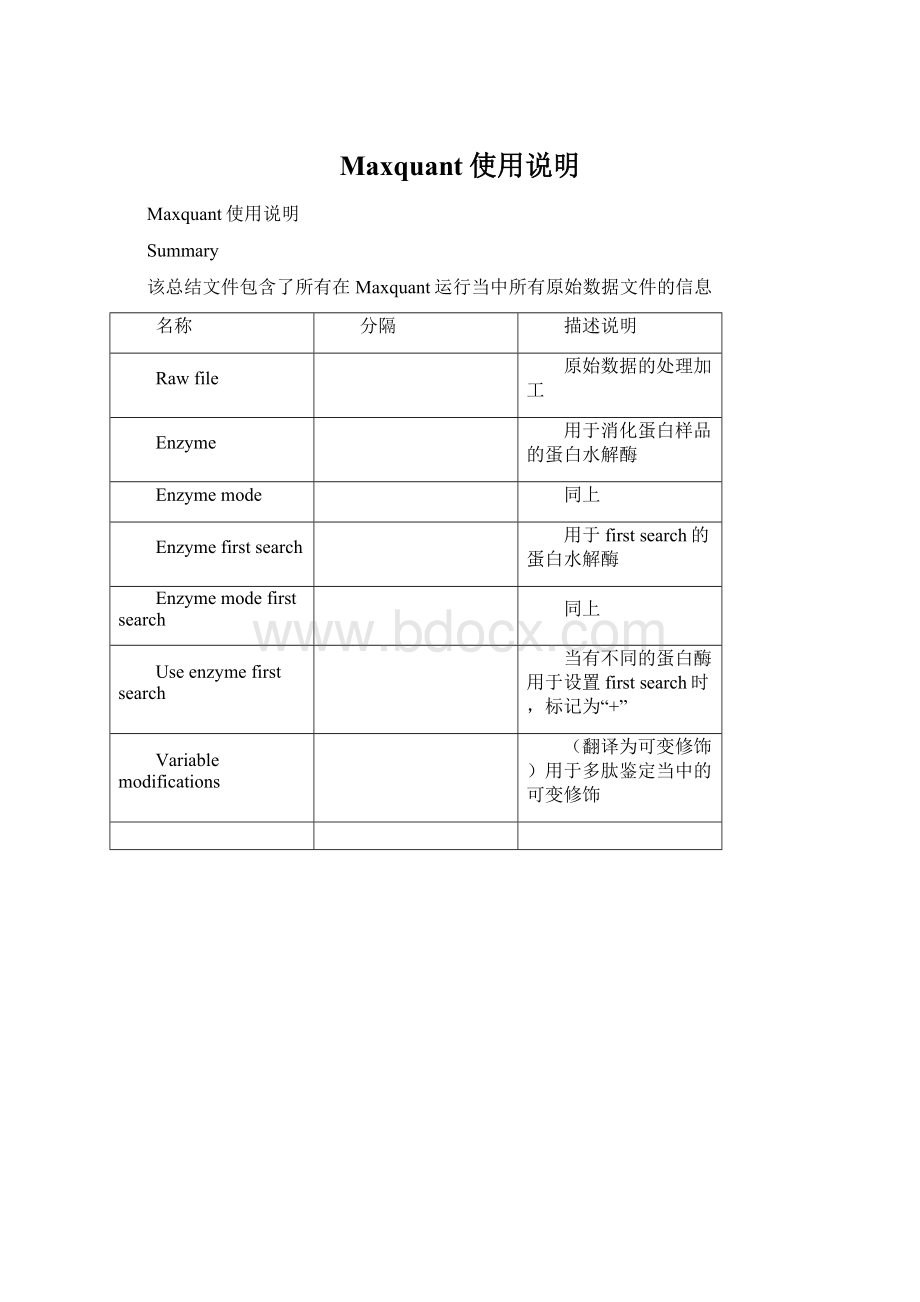
Maxquant使用说明
Maxquant使用说明
Summary
该总结文件包含了所有在Maxquant运行当中所有原始数据文件的信息
名称
分隔
描述说明
Rawfile
原始数据的处理加工
Enzyme
用于消化蛋白样品的蛋白水解酶
Enzymemode
同上
Enzymefirstsearch
用于firstsearch的蛋白水解酶
Enzymemodefirstsearch
同上
Useenzymefirstsearch
当有不同的蛋白酶用于设置firstsearch时,标记为“+”
Variablemodifications
(翻译为可变修饰)用于多肽鉴定当中的可变修饰
Time-dependentrecalibration
时间依赖性的再校准:
当出现该校准时,数据框内标记为“+”,时间依赖性的校准用于提高数据的质量
MS
在原始数据当中的MS1记录的数据量
MS/MS
在原始数据当中的MS2记录的数据量
MS3
在原始数据当中的MS3记录的数据量
MS/MSsubmitted
用于软件分析的串联的MS的数量
MS/MSsubmitted(SIL)
用于软件分析的串联的MS的数量,这里检测的是作为标记簇(重标组,labelingcluster)的母离子被检测。
MS/MSsubmitted(ISO)
用于软件分析的串联的MS的数量,这里检测的是作为同位素模式的母离子被检测。
MS/MSsubmitted(PEAK)
用于软件分析的串联的MS的数量,这里检测的是作为单个峰(singlepeak,这里的单个峰的意思应该是没有同位素峰)的母离子被检测。
MS/MSidentified
鉴定到的串联质谱数的总数量
MS/MSidentified(SIL)
鉴定到的串联质谱数的总数量,这里检测的是作为标记簇(重标组,labelingcluster)的母离子被检测。
MS/MSidentified(ISO)
鉴定到的串联质谱数的总数量,这里检测的是作为同位素模式的母离子被检测。
MS/MSidentified(PEAK)
鉴定到的串联质谱数的总数量,这里检测的是作为单个峰(singlepeak,这里的单个峰的意思应该是没有同位素峰)的母离子被检测。
MS/MSidentified[%]
被鉴定到的串联质谱的比例
MS/MSidentified(SIL)[%]
被鉴定到的串联质谱的比例,这里检测的是作为标记簇(重标组,labelingcluster)的母离子被检测。
MS/MSidentified(ISO)[%]
被鉴定到的串联质谱的比例,这里检测的是作为同位素模式的母离子被检测。
MS/MSidentified(PEAK)[%]
被鉴定到的串联质谱的比例,这里检测的是作为单个峰(singlepeak,这里的单个峰的意思应该是没有同位素峰)的母离子被检测。
PeptideSequencesIdentified
通过记录在二级质谱上的谱图而鉴定出来的氨基酸序列的多肽的总数量
Peaks
被检测到的MS1(fullscans)的总数量
PeaksSequenced
通过MS2测出氨基酸序列的多肽的总数量
PeaksSequenced[%]
通过MS2测出氨基酸序列的多肽的比例(这里指的应该是串联质谱鉴定到的多肽的数量与MS1鉴定到的数量之比)
PeaksRepeatedlySequenced
在二级质谱当中被重复鉴定的次数(超过1次)
PeaksRepeatedlySequenced[%]
在二级质谱当中被重复鉴定的多肽的数量站总鉴定多肽数量的比率
IsotopePatterns
检测到的同位素峰的总数量
IsotopePatternsSequenced
被二级质谱(测序)鉴定到的同位素序列的总数量
IsotopePatternsSequenced(z>1)
被二级质谱(测序)鉴定到的同位素序列的总数量(电荷数>1)
IsotopePatternsSequenced[%]
被二级质谱(测序)鉴定到的同位素序列的比例
IsotopePatternsSequenced(z>1)[%]
被二级质谱(测序)鉴定到的同位素序列的比例(电荷数>1)
IsotopePatternsRepeatedly
Sequenced
用串联质谱对同位素重复(超过1次)测序的总数量
IsotopePatternsRepeatedly
Sequenced[%]
用串联质谱对同位素重复(超过1次)测序的比率
Recalibrated
重新校准:
当原始数据当中的质量被重新校准时,会在该框下显示“+”
Av.AbsoluteMassDeviation[ppm]
被鉴定的多肽和数据库当中的多肽对比后,其检测质量与理论质量偏差的平均值,单位为百万分之一
MassStandardDeviation[ppm]
被鉴定的多肽和数据库当中的多肽对比后,其检测质量与理论质量偏差的标准差,单位为百万分之一
Av.AbsoluteMassDeviation[mDa]
被鉴定的多肽和数据库当中的多肽对比后,其检测质量与理论质量偏差的平均值,单位为百万分之一道尔顿
MassStandardDeviation[mDa]
被鉴定的多肽和数据库当中的多肽对比后,其检测质量与理论质量偏差的标准差,单位为百万分之一道尔顿
Labelfreenormparam
用于label-free实验当中测定峰强度值的标准因素
Evidence
名称
分隔
描述说明
Sequence
鉴定出来的多肽的序列
Length
保存在sequence框内的序列长度
Modifications
在被鉴定的多肽上的转录后修饰
Modifiedsequence
包含修饰位点的多肽序列,修饰位点会标记在被修饰的氨基酸前面,修饰方式会以缩写的形式呈现出来,一般情况下,多肽会被下划线标记
Carbamidomethyl(C)Probabilities
半胱氨酸被烷基化的可能性:
包含翻译后修饰的多肽可能出现修饰的可能性,其中概率为0—1其中1为最大,该列表示半胱氨酸烷基化的可能性
Oxidation(M)Probabilities
甲硫氨酸氧化的可能性:
包含翻译后修饰的多肽可能出现修饰的可能性,其中概率为0—1其中1为最大,该列表示甲硫氨酸氧化的可能性
Carbamidomethyl(C)ScoreDiffs
通过计算PTM添加到的那个位置以及没有PTM位点之间的差异计算,如果值为负,则说明其修饰的可能性近乎没有
Oxidation(M)ScoreDiffs
通过计算PTM添加到的那个位置以及没有PTM位点之间的差异计算,如果值为负,则说明其修饰的可能性近乎没有
Acetyl(ProteinN-term)
发生在蛋白质N末端的乙酰化的数量
Carbamidomethyl(C)
发生在半胱氨酸上的烷基化修饰的数量
Oxidation(M)
发生在甲硫氨酸上的氧化修饰的数量
Missedcleavages
水解酶漏切多肽的数量
Proteins
根据多肽而推断出来的蛋白质的名称
Leadingproteins
Leadingrazorprotein
Genenames
Proteinnames
Type
Rawfile
MS/MSm/z
Charge
m/z
Mass
Resolution
Uncalibrated-Calibratedm/z[ppm]
Uncalibrated-Calibratedm/z[Da]
Masserror[ppm]
Masserror[Da]
Uncalibratedmasserror[ppm]
Uncalibratedmasserror[Da]
Maxintensitym/z0
Retentiontime
Retentionlength
Calibratedretentiontime
Calibratedretentiontimestart
Calibratedretentiontimefinish
Retentiontimecalibration
Matchtimedifference
Matchm/zdifference
Matchq-value
Matchscore
Numberofdatapoints
Numberofscans
Numberofisotopicpeaks
PIF
Fractionoftotalspectrum
Basepeakfraction
PEP
MS/MScount
MS/MSscannumber
Score
Deltascore
Combinatorics
Intensity
Reverse
Potentialcontaminant
id
ProteingroupIDs
PeptideID
Mod.peptideID
MS/MSIDs
BestMS/MS
AIFMS/MSIDs
Carbamidomethyl(C)siteIDs
Oxidation(M)siteIDs
- 配套讲稿:
如PPT文件的首页显示word图标,表示该PPT已包含配套word讲稿。双击word图标可打开word文档。
- 特殊限制:
部分文档作品中含有的国旗、国徽等图片,仅作为作品整体效果示例展示,禁止商用。设计者仅对作品中独创性部分享有著作权。
- 关 键 词:
- Maxquant 使用说明
 冰豆网所有资源均是用户自行上传分享,仅供网友学习交流,未经上传用户书面授权,请勿作他用。
冰豆网所有资源均是用户自行上传分享,仅供网友学习交流,未经上传用户书面授权,请勿作他用。


 《雷雨》中的蘩漪人物形象分析 1.docx
《雷雨》中的蘩漪人物形象分析 1.docx
